片段分析仪助力食道癌综合性RNA数据集分析研究
食道癌(EAC)是全球第六高致死率的癌症。巴雷特食管症(NDB)是已知的EAC前体病变,表现为食管的正常鳞状粘膜被柱状上皮覆盖。其可经历低度异性增生(LGD)到高度异型增生(HGD),最终发展到食道癌。在过去的几十年里,食道癌的发病率急剧增加。因此迫切的需要更好地了解疾病的病因,并识别新的预后和预测性生物标志物,以提高患病的生存概率。在本文中,科学家们选取了17位不同的食道癌患者的样本,进行了综合的数据分析。基于这些数据,共形成了3种生物型,共有119个表达谱,包括miRNA(51)、mRNA(51)和circRNA(17)。善用这种独特的数据资源,有助于发现新的生物标志物和疾病机制,进行组织和液体活检的比较,整合编码和非编码RNA模式,此外还可以作为其他基于RNA研究的验证方式。此外,在该数据集中还可以识别出结构RNA的差异,包括蛋白质编码突变、融合基因和环状RNA。该文由比利时根特大学Katleen De Preter团队于2022年3月在Nature 子刊scientific data 上发表。
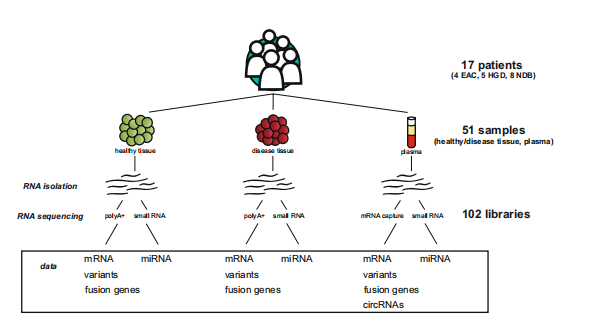
图 1 实验线路设计
实验方法:
患者样本收集
该项目收集4名食道癌患者(EAC),5名高度异型增生患者(HGD)和8名非增生巴雷特食道症患者(NDB)的共51份血液组织样本。所用样本均在治疗前采集。组织样本是在内镜检查(NDB和HGD)或肿瘤手术切除(EAC)期间获得的。从病变组织区收集至少一个组织样本被送去进行病理检查。若收集到非目标疾病或健康样本则会使用RNAlater(Qiagen 76104 RNA保存液)进行长期保存。血液样本使用6 ml EDTA管收集,然后用9 ml柠檬酸钠(3.2%)真空血管进行采血。1800g离心10 min制备血浆
RNA提取
组织样本:采用miRNeasy mini kit (Qiagen 货号217004)抽提总RNA。提取后的RNA由QUBIT进行浓度测定,由安捷伦片段化分析仪进行RNA 完整性质控。其中高达70.6%的样本的RNA完整性水平大于质控数字指标7,表示质量较好。
血浆样本:采用miRNeasy Serum/Plasma Kit (Qiagen 货号217184)提取RNA,其中用来mRNA捕获测序的样本还进行gDNA去除。
测序
组织样本:PolyA+ RNA 测序
采用TruSeq Stranded mRNA Library Prep kit (Illumina)进行测序文库构建,上样量为100 ng。用安捷伦片段化分析仪进行文库质控,终文库在NextSeq 500(Illumina)仪器上进行paired-end测序。
血浆样本:mRNA捕获测序
使用TruSeq RNA Access Library Prep Kit (Illumina,现已更名为TruSeq RNA Exome)进行文库制备,上样量为8.5 µl RNA洗脱液。使用安捷伦片段化分析仪进行文库质控。样品在NextSeq 500(Illumina)仪器上进行paired-end测序。对所有样本进行了两次测序,以获得适当的测序深度。
Small RNA 测序
使用NEBNext small RNA library prep kit进行文库制备,上样量为100 ng (组织样本)和 6 µl 总RNA(血浆样本)。采用Pippin Prep系统,选择含有成熟miRNAs(~147-157nt片段)文库根据qPCR定量进行归一化并进行汇总,并且用乙醇沉淀浓缩,用Qubit 2.0荧光仪定量。在NextSeq 500(Illumina)仪器上对组织和血浆样本进行单端测序。
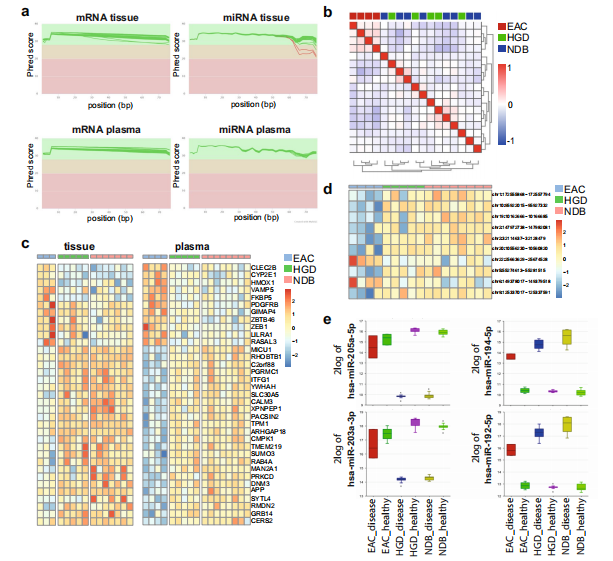
图 2 数据的技术验证 a)RNA原始reads测序数据的质量图:mRNA组织和血浆数据的每个碱基平均质量(上行),以及miRNA组织和血浆数据(下行); b)基于皮尔逊相关系数的mRNA血浆样本的分层聚类,显示了EAC样本与HGD和NDB样本的聚类; c)热图显示组织(左)和血浆(右)样本中35个重叠的不同表达基因(上下)的相对表达量; d)血浆中十大丰富环状RNA的相对表达(EAC vs NDB); e)与匹配的健康食管组织相比,四种最常见的EAC、HGD和/或NDB组织样本中上调和下调的miRNAs
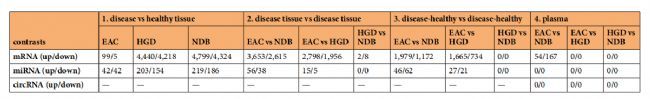
表 1 组织样本(包括19734个基因和676个miRNAs)和血浆样本(11255个基因,457个miRNAs和2275个环状RNA)的表达和丰度分析结果
结论:
1、基因表达和丰度分析
对组织和血浆中的mRNA、miRNA和环状RNA进行了同源基因表达和丰度分析。不同表达基因的数量见表1。预处理后的数据也被上传到R2 Genomics Analysis and Visualization Platform 中(http://r2.amc.nl),可对数据集的进一步探索和可视化。在本研究中,我们在EAC、HGD和NDB患者的血浆中鉴定了几种环状RNA,它们的环状结构更能抵抗外切酶的RNA降解,因此这种类型的RNA作为循环生物标记物具有很大的潜力。虽然我们关注使用小RNA测序数据进行miRNA表达和丰度分析,但其他小RNA如tRNA(片段)和piRNA也可以使用我们的数据进行分析。
2、相关miRNA和mRNA的表达
该数据集包含了匹配疾病和健康组织样本的miRNA和mRNA数据。因此,我们在数据中可以研究miRNA和mRNA表达之间的关系。例如,已知Hedgehog(HH)信号通路在EAC和NDB60中发挥重要作用。在NDB中,hsa-miR-194表达的增加导致SUFU的丢失,从而导致Sonic Hegdgehog(SHH)基因的上调。在我们的NDB组织数据以及EAC和HGD组织样本中,也观察到与健康组织相比,hsa-miR-194和SHH的表达上调,以及SUFU的表达下调。这种独特的数据集可对疾病和健康部分数据进行匹配,以便进一步探索相关通路,即通过使用miRNA和mRNA数据。
3、突变分析
基于polyA+测序数据(组织)和mRNA捕获测序数据(血浆),进行突变分析。疾病特异性变异被严格筛选。随后,这些变异与血浆中的变异进行分析。在2例EAC患者、5例 HGD患者和4例NDB患者的血浆中,共发现了24个变异。每个患者发现1-7个变异,但在疾病组内或组间没有观察到重叠。根据前列腺癌(COSM5564582)、宫颈癌或胆道癌(COSM5493837)或大肠癌(COSM5756079)的COSMIC 数据库,树状变异是已知的肿瘤突变。这些结果证明了该数据集能够在血浆RNA测序数据中识别可能的体细胞突变或疾病特异性RNA编辑事件。
4、融合基因分析
EAC组织中融合基因分析的研究报道很少。在本文中,科学家们展示了检测EAC、HGD和NDB组织和血浆样本的融合基因的潜力。在组织样本中,在所有样本中都发现了潜在的融合基因。通过排除(在每个样本的基础上)在健康组织中也发现的融合基因,我们确定了疾病特异性的融合基因。对于所有的样本,有2-14个融合基因保留(不包括潜在的假阳性)。对于血浆样本,在一个HGD患者样本和两个NDB患者样本中识别出潜在的融合基因,其中有两个重叠的融合基因(ID5_HGD和ID19_NDB)。疾病组织与血浆样本之间没有融合基因的重叠。科学家们仍然需要进一步验证这些潜在相关的融合基因。
实验与分析
展源
何发
相关文章
-

AAS法分析茶叶中的铅,镉,砷
2020-05-27
-
红外光谱分析,你了解多少?
2021-01-11
-

三聚氰胺,你还要害多少人
2020-05-27
-

QC, IQC, IPQC, QA,到底是什么鬼?
2020-05-27
-

安捷伦与Proscia达成合作,以加速数据驱动的精准医疗
2023-03-13
-

HPLC检测器,你了解吗?
2024-03-06
-

超净工作台原理,使用与维护
2020-05-27
-

选对色谱柱,快速开发方法
2020-05-27
-

做PGS/MS分析时,如何防止焦油状污染物进入毛细柱
2020-05-27

加载更多